SPM - Theoretischer Hintergrund
SPM – statistical parametric mapping – ist eine
Software zum Berechnen von fMRI und PET-Daten und wurde vom Functional
Imaging Laboratory des Institute for
Cognitive Neurology,
Universität London entwickelt. Es handelte sich dabei nicht um ein
eigenständiges Programm sondern vielmehr um eine MATLAB –Applikation, die unter
einer eigenen Oberfläche läuft. SPM ist kostenlos im Internet unter http://www.fil.ion.ucl.ac.uk/spm/
erhältlich, MATLAB ist eine mathematische Software, die kommerziell vertrieben
wird und für das Arbeiten mit SPM unentbehrlich ist.
SPM benötigt die Daten in
folgender Orientierung:
X-Achse: Zunahme von Links nach Rechts
Z-Achse: Zunahme von Inferior nach Superior
Die Analyse der fMRI-Daten unterteilt sich in mehrere Arbeitsschritte.
Im
ersten Komplex, dem Daten-Preprocessing werden die
Daten für die statistische Auswertung vorbereitet, von Bewegungsartefakten, und
Signalsprüngen befreit und in den stereotaktischen Raum nach Talairach übertragen. Zum Preprocessing gehören:
![]() Coregistrierung
& Realignment
Coregistrierung
& Realignment
![]() Normalisierung
Normalisierung
![]() Smoothen
Smoothen
Dem Preprocessing folgt die
Definition des statistischen Modells und die statistische Analyse der Daten:
![]() Erstellung des statistischen Modells
Erstellung des statistischen Modells
![]() Statistische Auswertung
Statistische Auswertung
![]() graphische Darstellung der Ergebnisse
graphische Darstellung der Ergebnisse
Für die
korrekte graphische Darstellung der Ergebnisse ist es notwendig, neben den
eigentlichen fMRI-Daten auch noch ein hochaufgelösten
3D-MPR-Datensatz aufzunehmen.
1.
Coregistrierung
Es gibt
2 Formen des Coregistrierens: zum einen wird im
Rahmen der Bewegungskorrektur coregistriert:
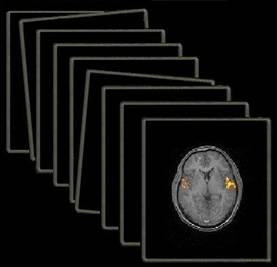
![]() jede fMRI Messung hat bis zu 120 oder mehr Einzelbilder
jede fMRI Messung hat bis zu 120 oder mehr Einzelbilder
![]() daraus wir ein Gesamtbild
errechnet
daraus wir ein Gesamtbild
errechnet
![]() durch Bewegungsartefakte sind Einzelbilder
aber nicht immer Deckungsgleich
durch Bewegungsartefakte sind Einzelbilder
aber nicht immer Deckungsgleich
![]() durch die Coregistrierung
wird jedes Einzelbild im Raum genau in seiner Position definiert dadurch werden
die Verschiebungen der Einzelbilder errechnet
durch die Coregistrierung
wird jedes Einzelbild im Raum genau in seiner Position definiert dadurch werden
die Verschiebungen der Einzelbilder errechnet
![]() Anhand dieser Daten wird die
Bewegungskorrektur durchgeführt
Anhand dieser Daten wird die
Bewegungskorrektur durchgeführt
Die
zweite Form des Coregistrierens dient der
Fusionierung der Bilder unterschiedlicher Modalitäten wie fMRI-EPI-Bildern
und 3D-MPR-Bildern.
2.
Realign (Bewegungskorrektur)

![]() das erste Bild der Zeitserie dient
dabei als Referenzbild
das erste Bild der Zeitserie dient
dabei als Referenzbild
![]() alle anderen Bilder werden daran ausgerichtet
und zur Deckung gebracht (Rigid Body-Transformation)
alle anderen Bilder werden daran ausgerichtet
und zur Deckung gebracht (Rigid Body-Transformation)
![]() Verschiebungen bis zu 2mm und 0,5° können von
der Software korrigiert werden
Verschiebungen bis zu 2mm und 0,5° können von
der Software korrigiert werden
Die
Bewegungskorrektur hat für die Auswertung eine elementare Bedeutung da schon
geringe Bewegungsartefakte Aktivierungen vortäuschen können, die von den
gesuchten Aktivierungen nicht unterschieden werden können. Auf Grund der Dauer
der Untersuchung (mehrere Minuten) ist eine 100%ig Fixierung des Kopfes jedoch
nicht möglich. Hinzu kommen noch Artefakte, die durch physiologische Parameter
(z.B. Atmung / Herzschlag), die Messung und das Paradigma (z.B.
stimuluskorrelierte Bewegungen) bedingt sind. Deshalb können nur Datensätze zur
Auswertung heran gezogen werden, deren Bewegungsartefakte nicht größer als 2mm
in den 3 Raumachsen bzw. 0.5° Rotation um diese Achsen sind. SPM zeigt diese
Daten nach der Bewegungskorrektur an à immer
kontrollieren!
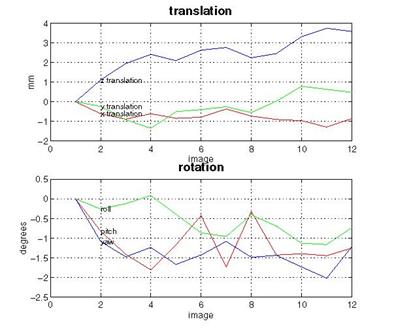
![]() die nebenstehenden Daten zeigen deutliche
Bewegungsartefakte >2mm und >0,5°, die durch die Software nicht
korrigierbar sind.
die nebenstehenden Daten zeigen deutliche
Bewegungsartefakte >2mm und >0,5°, die durch die Software nicht
korrigierbar sind.
![]() dieser Datensatz muss von der weiteren
Auswertung ausgeschlossen werden, da nicht mehr mit Sicherheit ausgeschlossen
werden kann, dass die gefundenen Aktivierungen nicht auf die nicht
korrigierbaren Bewegungen zurück geführt werden können
dieser Datensatz muss von der weiteren
Auswertung ausgeschlossen werden, da nicht mehr mit Sicherheit ausgeschlossen
werden kann, dass die gefundenen Aktivierungen nicht auf die nicht
korrigierbaren Bewegungen zurück geführt werden können
3.
Normalisierung
Die individuelle Anatomie ist zum
Teil sehr unterschiedlich. Durch die Normalisierung wird die individuelle
Anatomie auf einen standartisierten Raum, das Talairach - Koordinaten-System, angepasst (nichtlineare
Transformation in den Standardraum nach Talairach)
Somit liegen die gleichen anatomische Strukturen immer an den selben Koordinaten.
Dadurch ist der Vergleich der Ergebnisse innerhalb und zwischen
Untersuchungs-Gruppen möglich. Für die Einzelfallanalyse ist die Normalisierung
nicht notwendig, nicht normalisierte Daten sind aber nicht direkt vergleichbar.
Durch die Normalisierung kommt es zu Abweichungen von der individuelle Anatomie
à für
genaue individuelle anatomische Lokalisation (z.B. in der Neurochirurgie) keine
Normalisierung verwenden.
4.
Smoothen (Glätten)
Durch
das Smoothen werden große Signalsprünge innerhalb der
Datensätze eliminiert (geglättet). Ziel ist, das Signal-Rausch-Verhältnis zu
verbessern. Dadurch können die echten Aktivierungen besser von Störsignalen
abgegrenzt werden.
Beim smoothen wird die Verknüpfung eines Bildpunktes mit
benachbarten Bildpunkten bewertet. Die Festlegung der Bewertung der
Nachbarschaft erfolgt durch eine Filtermaske (Kernel).
5.
Statistisches Modell
und Auswertung
Mit dem Smoothen ist das Daten-Preprocessing abgeschlossen. Nun wird das statistische
Model (Design-Matrix) erstellt. Hier fließen die Information des Paradigmas ein
(Anzahl der Bilder, Interscanninterval, Anzahl und
Länge der ON/OFF-Phasen, Anzahl der Trails usw.) und es werden Hoch- und Tiefpassfilter
definiert. Die Statistik basiert auf einer Voxel by
Voxel t-/F-Test-Statistik., d.h. für jedes Voxel wird ein univariater
Standarttest auf Signifikanz durchgeführt.
6.
Graphische
Ergebnisdarstellung
Um die Ergebnisse graphisch darstellen zu können, müssen
noch die mitgemessenen 3D-MPR-Datensätze das entsprechende Preprocessing
durchlaufen. Dabei werden die anatomisch hochaufgelösten Daten mit den
fMRI-EPI-Daten coregistriert (d.h. sie werden
einander „angepasst“ und nachfolgend auch normalisiert, sofern auch die
fMRI-EPI-Daten normalisiert wurden). Danach können die Aktivierungen den
anatomischen Bildern überlagert werden und genau anatomisch lokalisieren
werden.
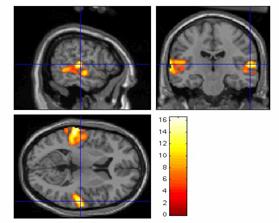
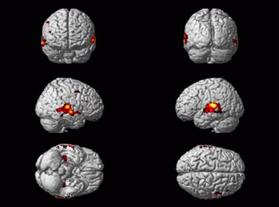
Es gibt 2 Möglichkeiten der Darstellung:
Volume-Rendering:
Surface-Rendering
In den folgenden SPM-Kapiteln
soll beispielhaft eine einfache Single-Subjektanalyse gezeigt werden um einen
Einstieg in die Auswertung zu geben. Erfahrungsgemäß tut sich gerade der SPM-Anfänger recht schwer die ersten Datensätze
auszuwerten. Es bedarf schon ein wenig Zeit und leistungsfähiger Computer um
tiefer in die Auswertung vorzudringen. Ziel von www.fmri-easy.de
ist diesen Einstig etwas zu erleichtern. Ausführliche weiterführende
Informationen zu diesem Thema gibt es in englischer Sprache unter: http://www.fil.ion.ucl.ac.uk/spm/
